バイオストリーム株式会社より研究支援ツールのご案内
明瞭でフェーズ問題解消のHLAタイピング NGS解析によるシングルアッセイ
CareDx TruSight HLA v2 イルミナ社製NGSベースのHLAタイピングキット
- 包括的アッセイ:シングルアッセイで、11のHLA遺伝子座の高分解能シーケンシングが可能
- 明瞭な結果:ディープシークエンシングにより、正確で明瞭なHLAタイピングが可能
- ”DNAから結果” のトータルソリューション:ライブラリの調整、イルミナシーケンシング、TruSight HLA Assign 2.1ソフトウェア によるデータ解析までの完結
製品の詳細
見出し 説明文概要 - TruSight HLA ワークフロー
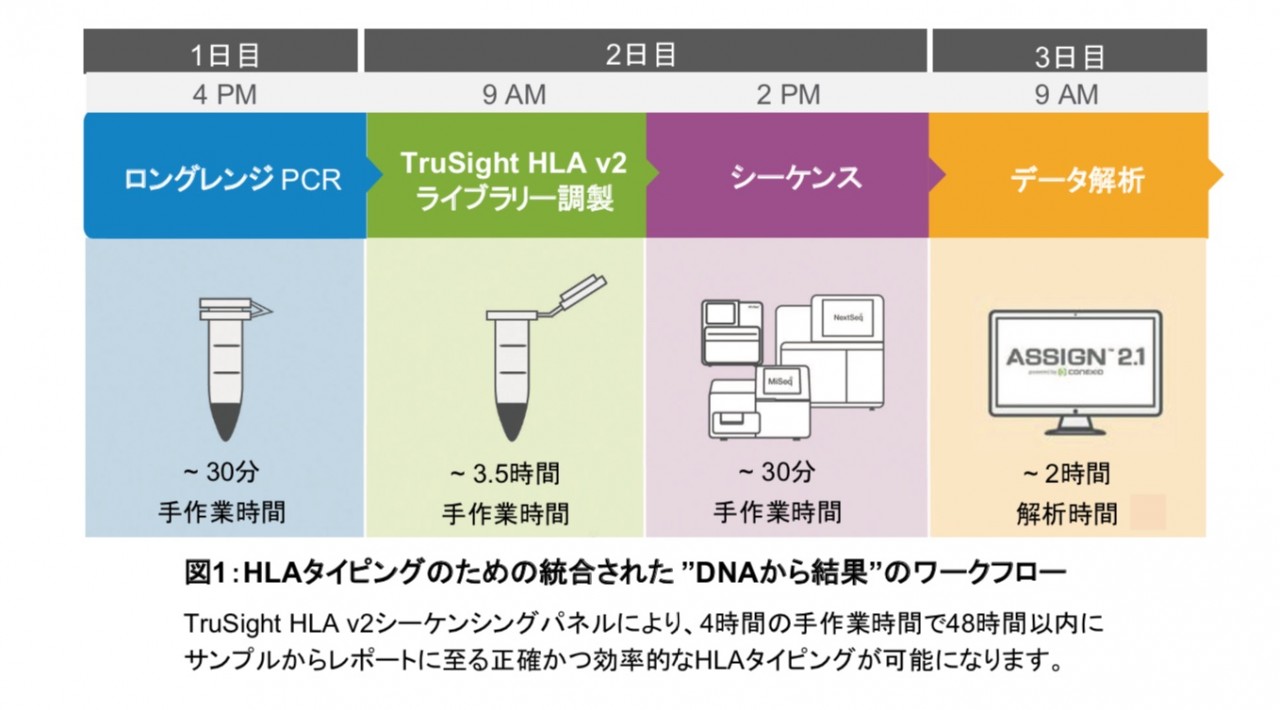
図1
完全なHLA遺伝子配列の取得
TruSight HLA v2 シーケンシングパネルは、一般的にタイプされている全てのHLA遺伝子座と新たな関連性 のある遺伝子座をカバーしています(表1)。この拡張された遺伝子カバレッジにより、従来からの遺伝子座(クラ スIエキソン2,3および4;およびクラスIIエキソン2および3)を超えて、より高分解能のタイピングのためのさらなる 情報が得られます。さらに、TruSight HLA v2 パネルは完全な遺伝子カバレッジを達成し、新たなプライマーを 設計する必要なく新しい対立遺伝子の発見を可能にします。
TruSight HLA v2 パネルタイプ 11 HLA 遺伝子座
| 遺伝子座 | ターゲット シーケンス |
|---|---|
| HLA-A | 4.1 kb (全遺伝子) |
| HLA-B | 2.8 kb (エクソン 1 – イントロン 6) |
| HLA-C | 4.2 kb (全遺伝子) |
| HLA-DRB1/3/4/5 | 4.6 kb – 5.1 kb (エクソン 2 – イントロン 4) |
| HLA-DQB1 | 6.9 kb (全遺伝子) |
| HLA-DPB1 | 9.7 kb (エクソン 2 – 3’ UTR) |
| HLA-DQA1 | 7.3 kb (全遺伝子) |
| HLA-DPA1 | 10.3 kb (全遺伝子) |
ライブラリー調整のための最先端のNGSケミストリ
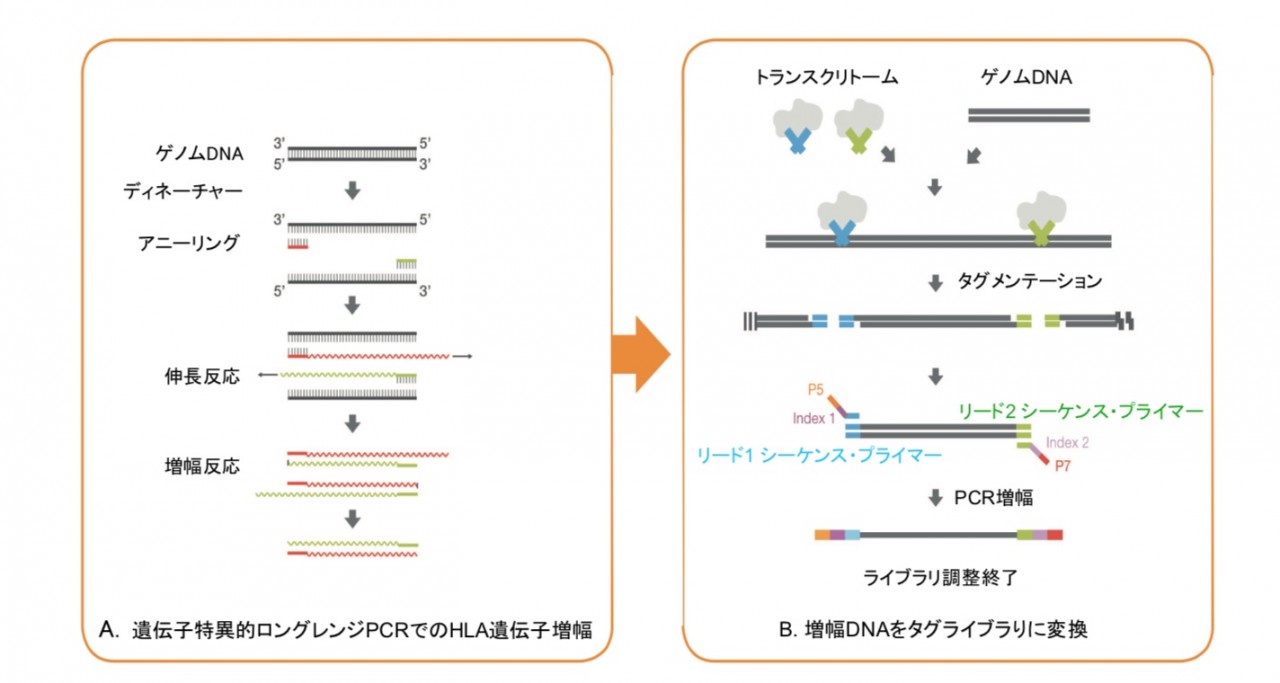
TruSight HLA v2 シーケンシングパネルは、ロングレンジPCRおよびHLA特異的Nexteraライブラリー調製 法を用いて、高精度で明瞭なHLAタイピングをシングルアッセイで作成します(図2)。 さらに、ユニークなマ ルチプレックス機能と統合されたサンプルバーコードにより、最大384サンプルを同時に分析するためのサン プルプーリングが可能になります。 TruSight HLA v2のワークフローは、ロングレンジPCR(図2A)での遺伝子座特異的プライマーを用いたHLA 遺伝子の増幅から始まります。 次に、ラピッドNexteraライブラリー調製ステップでは、増幅されたDNA断片 にアダプタータグを付加し(図2B)、一般的な末端修復処理を必要としません。
図2
イルミナのデスクトップシーケンサーとの多彩な シーケンシングオプション
調製されたライブラリーは、シーケンシングのためにMiniSeqTM、MiSeq、またはNextSeqシステムに直接 ロードします(図4)。 HLA遺伝子座は、高品質にペアエンド 2×150bp の読み取りでシーケンスされ、高密度 多型を使用して正確にフェーズを割り当てることを可能にします。これにより、明瞭なHLAタイピング結果を シーケンシングデータから直接得ることができます。 サンプルから結果まで、工程は48時間以内に完了します。
TruSight HLA Assign 2.1 ソフトウェアによる 最適化されたデータ解析
このソフトウェアは、TruSight HLA v2 ライブラリから得られたシーケンスデータを解析します。 各サンプルの HLAアンプリコンを1つのバーコードライブラリーにプールし、1サンプルにつき1対のFASTQファイルが得られ ます。デマルチプレクスとFASTQファイルの生成後、ファイルはTruSight HLA Assign 2.1ソフトウェアに直接 移行され、アライメントされます。
最初のアライメントの後、全てのヘテロ接合体位置はフェーズされます。フェーズされたアライメントは、国際 ImMunoGeneTics情報システム(IMGT)/ HLAデータベース8に対して参照され、信頼性の高いHLAタイピン グ結果が生成されます。Assignソフトウェアは、 TruSight HLA v2 シーケンシングパネル専用に最適化され ています。これは、複数のサンプルおよび遺伝子座からのシーケンスを、以下のユーザーフレンドリーなイン ターフェースへのインポートを可能にします。
- より詳細な分析を必要とする遺伝子座の迅速な同定のための統一された表示でのパネ ルサマリー
- 最もよく一致した対立遺伝子のパネル表示で、関連する(一般的でよく報告されている) CWD対立遺伝子を検索することなく、まれな対立遺伝子の迅速な確認が可能
- 外部リソースやツールの必要性を軽減し、詳細な分析のための豊富なールセットを使用 して、配列、アライメント、およびレファランス・ビューを作成
図3
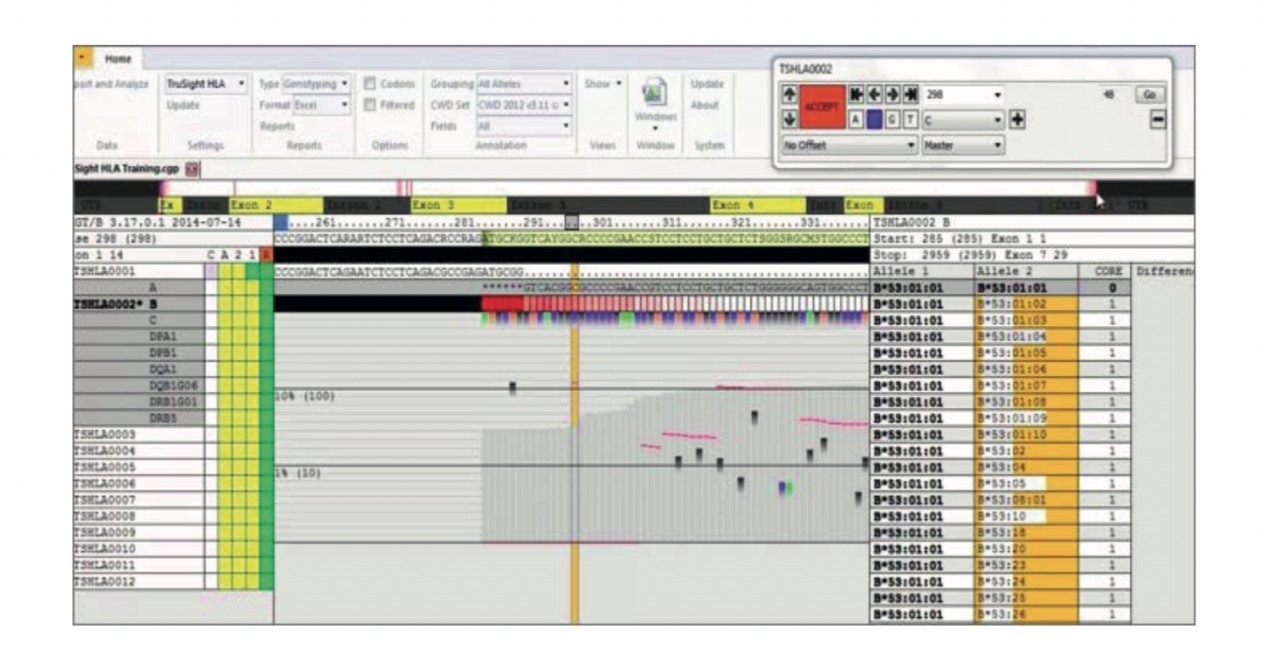
高精度HLAタイピング実証例
TruSight HLA v2 シーケンシングパネルで得られた高品質のタイピングを実証するために、合計959個の 参照対立遺伝子を含む72個のサンプルを、パネルを使用して精度とあいまいさの割合の解析について分析 しました。得られた結果は、以前の実験およびInternational Histocompatibility Working Group(IHWG)9 参照パネル(表2)で示されている別法でのタイピング結果と比較しました。比較実証のために、種々の提供 源からのサンプルを使用しました。
結 果
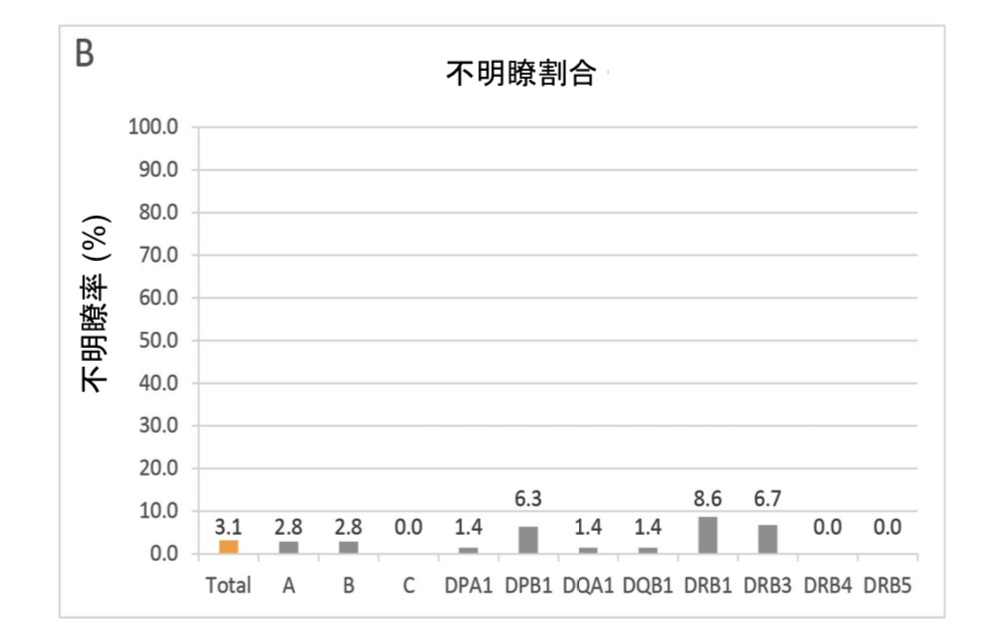
TruSight HLA v2のタイピング結果は、レファレンスパネルと比較して高い正確度(図5A)を示しています。72 サンプルのうち、959の対立遺伝子が一致度と精度の計算に利用可能なレファレンス タイピングとして発表 されており、907個(94.58%)の対立遺伝子がレファレンス タイピングと一致し、42個(4.38%)のレファラン スが増加したカバレッジや文献参照、または両方から修正されて、結果が正確であことが示されており、 5(0.52%)の対立遺伝子は新規エキソン変異体を有し、5(0.52%)対立遺伝子は1〜3塩基位置の編集を必 要とし、これらの最後の5つの対立遺伝子は正確ではないと考えられます。不明瞭率は、この研究でタイプさ れたすべての1294対立遺伝子を用いて計算され、結果として不明瞭率は3.17%でした(図5B)。
図4
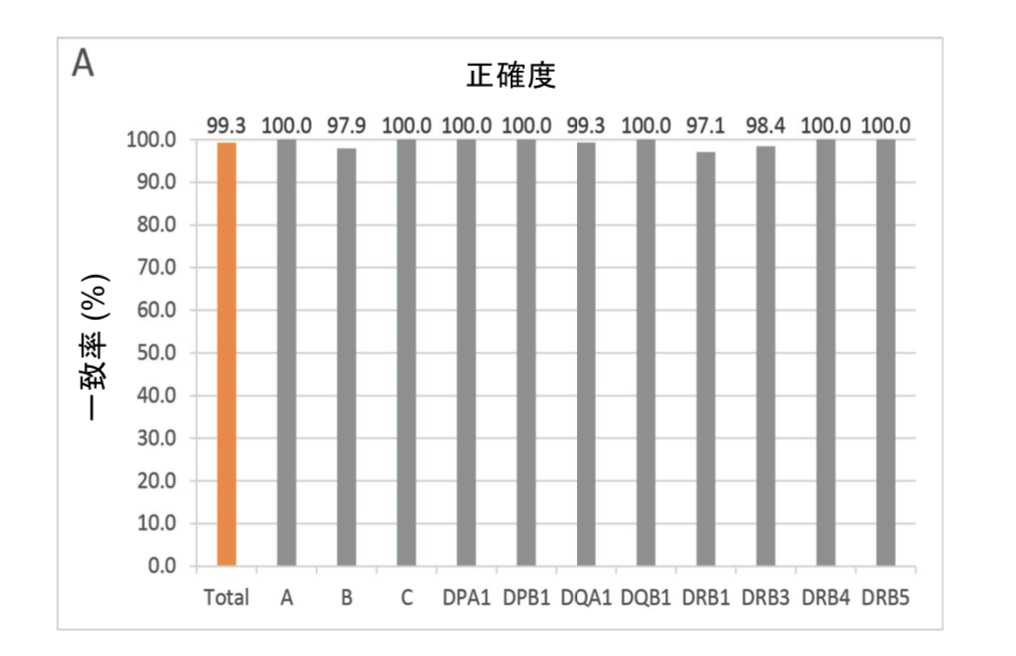
図5:TruSight HLA v2 パネルのタイピング性能
TruSight HLA v2 のタイピング結果は、利用可能なレファレンスタイピング結果 と比較して高い精度(A)と低いあいまい性(B)を示しています。
お役立ち資料

CareDx TruSight HLA v2 カタログ

CareDx Olerup QTYPE11 カタログ