インフォコム株式会社より研究支援ツールのご案内
TCR/BCRレパトア解析におけるゴールドスタンダード
MiXCR 免疫レパトア解析ソフトウェア
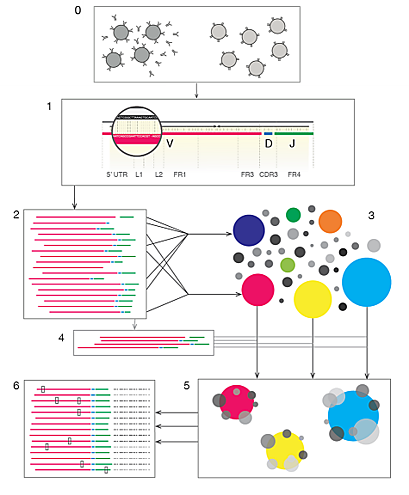
- 高い汎用性 : 既存のサンプル調製プロトコルによって得られたほぼ全てのデータに利用可能
- 高い検出感度 : 最適化されたアライメントアルゴリズムによりデータセットの情報を抽出
- ロバストな解析 : PCRやシーケンシングから生じるエラー修正し、クロノタイプを組み立て
- 詳細情報の提供 : アセンブルされたクロノタイプとアライメントに関する包括的な情報をご提供
- シンプルな操作性 : 典型的な分析においてはパラメーター設定が不要
- 解析の柔軟性 : 柔軟性に富んだ解析のカスタマイズが可能
☆☆ 1ヶ月間・無料トライアル実施中 ☆☆
MiXCR は、TCR/BCRレパトア解析におけるゴールドスタンダードとされ、ユーザーはサンプルから迅速かつ正確にあらゆるレパートリーを解析することが可能です。
試薬と組み合わせ免疫細胞の反応量を数値化できるため、従来よりも短時間かつ正確に対象となる抗体遺伝子を検出できます。
RNA-Seq・RepSeq・WGS・シングルセルデータ等から、レパートリーデータの抽出に対応しています。
製品の詳細
MiLaboratories製品ファミリーのレパトア解析フロー
MiLaboratories社製品は3つの製品で構成されています。「MIGEC」でNGS(次世代シーケンサー)から得られたシーケンスデータを読み込み、エラー修正を行います。つぎに「MiXCR」でクロノタイプの抽出を行い、「VDJtools」で結果のビジュアリゼーションや統計解析を行います。それぞれ単独でも利用可能です。
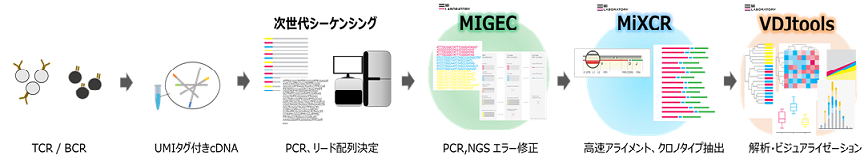
解析手順
MiXCRは以下の手順に沿って解析を行います。
- TCR/BCRの遺伝子配列データをセットします。
- シングル、ペアリードにおけるミスマッチ、挿入欠失を効率的に処理しアライメントを行います。
- 中間アライメント結果が抽出されます。
- 同一配列のものが同一クロノタイプとしてグルーピングされます。
- クオリティの低いシーケンスリードはさらなるマッピング用に収集されます。
- PCRとシーケンスエラーが修正されます。
- 最終的なクロノタイプがタブ区切りのファイルとして抽出されます。

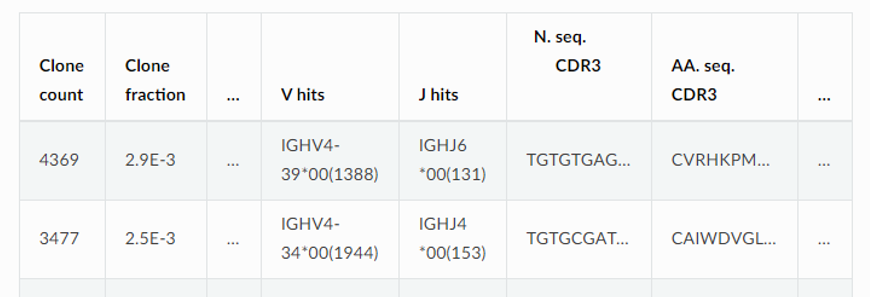
解析結果
MiXCRはfastqまたはfasta形式のファイルから、クロノタイプの情報(カウント数・フラクション・V遺伝子・J遺伝子・CDR3領域等)を出力します。
※一部列のみ抜粋
稼働環境
- OS: Java実行環境が利用可能な Windows、Linux、MAC OS X(いずれのOSもバージョンは問いません)
- Java Runtime Environment: バージョン 8 以上
- 空きメモリ: 1 - 16 GB (サンプルのクローン数に依存します)
文献情報
Bolotin D et al. MiXCR: software for comprehensive adaptive immunity profiling. Nature methods 12, no. 5 (2015): 380-381. doi:10.1038/nmeth.3364
お役立ち資料

MiLaboratories社3製品(MiXCR/MIGEC/VDJtools)カタログ


